在直播期间及直播结束有老师问道:LncRNA的qPCR引物如何设计?在设计的时候有没有需要特别注意的地方?如何能设计出最好的qPCR引物。基于这些问题,总结自己10年qPCR引物设计经验分享给大家。
LncRNA的qPCR引物相比于编码基因,是要复杂。导致其复杂的原因并不是引物设计原则上有特别之处,而是在于有太多的LncRNA数据库,数据库之间往往没有关联,且不同数据库的维护也不尽相同。今天的文章分两块:LncRNA数据库介绍和LncRNA引物设计注意事项。
LncRNA数据库介绍
1、NCBI RefSeq
NCBI不多做介绍,通常LncRNA信息我们参考RefSeq数据库中的数据,RefSeq数据库中的数据参考数据,是经过人工审核,其数据信息可信,注释全面。RefSeq数据库中LncRNA的命名通常是NR_或者XR_开头,后面加数字,其外显子信息位置,数量信息非常完整。关于RefSeq数据库的介绍,感兴趣的老师可以查看文章《带你走入RefSeq数据库》,链接https://mp.weixin.qq.com/s/ZuE40OSnzxrMk_yrP-Y5ag。
2、Ensembl
相同的LncRNA,Ensembl数据库中信息往往要比NCBI多很多,特别是转录本数量。且数据变化非常快且变化会很大,可能昨天浏览这个数据库中某个LncRNA只有2个转录本,隔天再去看的时候,可能就变成3个甚至更多。NCBI就不同,尽管更新频率也非常的快,但是LncRNA的变化通常很小,转录本数量基本不变化,序列变化的可能性也非常的小。关于不同数据中的命名格式可以查看文章《不知道数据库命名规则怎么能真正了解数据库?》链接https://mp.weixin.qq.com/s/D6r2CD1qKj0iMNdYSoqrKQ。
3、UCSC
UCSC数据库的LncRNA数据个人认为更新相对较慢,但有些LncRNA名称如uc001ylu就需要前往UCSC数据库查询其序列信息。UCSC Genome Browser可以根据基因组的位置、基因ID、转录本等信息进行浏览查询。

4、RNAcentral
RNAcentral 整合了包括 Ensembl、GENCODE、Greengenes、HGNC、LNCipedia、lncRNAdb、miRbase、NONCODE、RDP、RefSeq、Rfam、SILVA 在内的多个数据库。
5、NONCODE
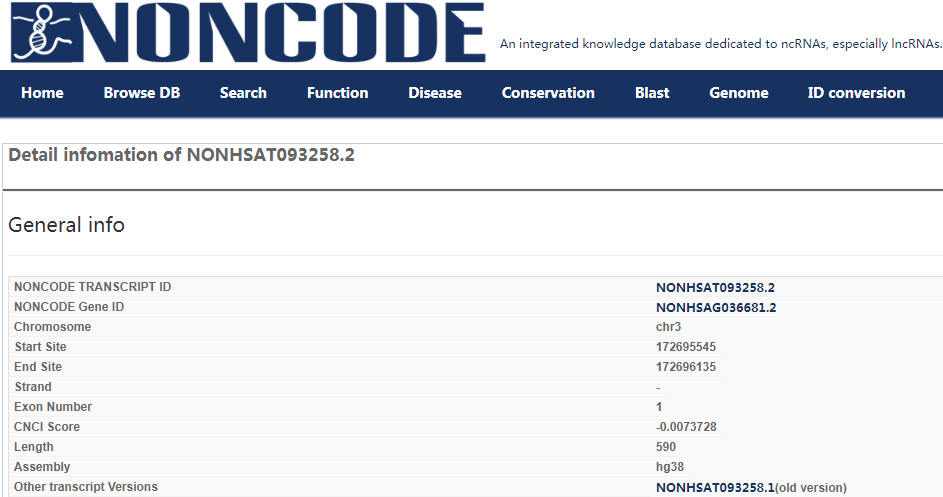
NONCODE是一款综合性的数据库,该数据库是一个比较全面的ncRNA相关注释的数据库,尤其是lncRNA信息,不仅支持常用lncRNA的Name、NONCODE Gene ID(例如:NONHSAG036681.2)搜索,部分lncRNA支持其他数据库名字进行搜索。该数据库目前收入了很多物种,主要是动物方面的,包括人、小鼠、大鼠、奶牛、鸡、果蝇、斑马鱼、线虫、酵母、拟南芥、黑猩猩、大猩猩、恒河猴、复鼠、鸭嘴兽、猩猩。数据库包含信息丰富,包括表达、功能、与疾病关系、染色体位置、序列保守性等,并可进行序列Blast搜索,同时支持数据下载。
6、Lncipedia
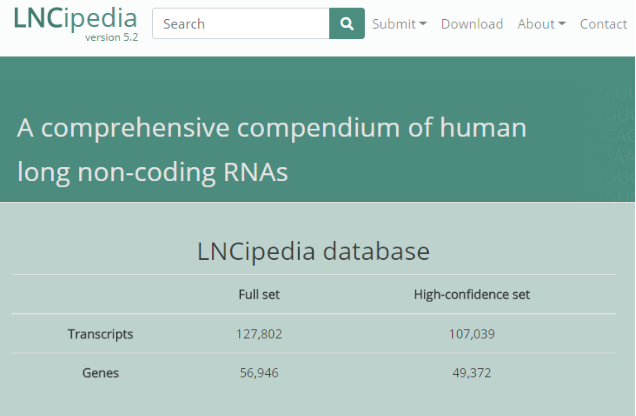
LNCipedia数据库整合了多个人类(Human)LncRNA数据库信息,很大程度上解决了LncRNA数据库各自为政的问题,这些数据库包括LncRNAdb、Broad Institute、Ensembl、Gencode、Refseq、NONCODE、FANTOM,同时还包括Nielsen, Hangauer等多篇文献中发现的LncRNA信息。目前已经更新到5.2版本,包括127,802 转录本序列和 56,946 条基因。
7、Lncrnadb
该数据库可以查询类似LINC00066, NCRNA00066名称的LncRNA。lncRNAdb数据库是一个真核生物的lncRNA综合数据库。它包括特异的序列结构信息,如转录本、基因组位置、表达、亚细胞定位和保守位点以及相关的功能和疾病。
数据库介绍总结:前面提到LncRNA的qPCR引物设计相比与编码基因确实要难,其原因就体现在LncRNA的数据库是在太多,而我们设计得到的qPCR引物通常都需要进行引物特异性比对,最好用的莫过于NCBI Primer-Blast,但是在特异性比对可供选择的比对数据库都只是NCBI,其他LncRNA数据库无法选择。接下来,小编就分享下非NCBI RefSeq来源的LncRNA的qPCR引物设计应该怎么做?
LncRNA 的qPCR引物设计注意事项
LncRNA的qPCR引物设计最主要的三个原则:跨外显子设计,特异性比对,引物位置。
1、跨外显子设计
跨外显子设计的目的就是避免基因组的污染,跨外显子设计有两种办法,具体见示意图:
(1)正向F引物和反向R引物落在不同的外显子上
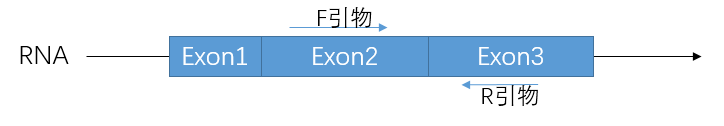
此处注意:(a)如果产物大小允许,正向F引物和反向R引物可以落在不同的外显子上;(b)如果正向F引物和反向R引物只能落在两个相邻的外显子上,那优先选择内含子最大的两个外显子上。
(2)正向引物或者反向引物跨了两个外显子

此处注意:(a)如果能选择(1)就不要选择(2)方法设计,(2)设计方法引物位置受限,设计得到的引物参数可能不是最优。(b)如果选择(2)方法设计,那跨两个外显子的引物的3端序列不要跨第二个外显子太多序列,建议不要超过6个碱基,否则就相当于没有跨外显子设计。
2、特异性比对
从上述数据库中查到LncRNA的序列信息后,建议先使用NCBI进行比对,简单做一个核苷酸比对和基因组比对。核苷酸比对的目的是看看这条LncRNA有没有与NCBI RefSeq同源性较高的序列信息。如果有,可能涉及到需要判断他们是否是同一条基因的问题。基因组比对的目的是简单判断其外显子个数组成,因为有些LncRNA数据库可能没有提供外显子数量信息和外显子位置信息。比对其实就是一个不同数据库之间LncRNA信息的转换,当统一后,那LncRNA引物设计就容易许多。
关于NCBI blast Database选择问题可以查看文章《使用NCBI做BLAST,我应该选择哪个Database?》,链接https://mp.weixin.qq.com/s/dKGH_GvNzhO_ofRTUuAbEQ。
3、引物位置
引物尽量不要落在LncRNA序列两端100bp序列以内,原因是防止两端序列不准确。曾经碰到一个老师,自己使用RACE验证Ensembl数据库中的LncRNA序列,发现两端序列有缺失。
4、同源区设计
本人设计qPCR引物通常都选择在同源区设计,检测其总RNA情况,具体根据各自实验要求而定。这里不多做展开介绍。
